I virus dell'Influenza Suina (SIV; sigla in inglese) appartengono al genere Influenzavirus tipo A della famiglia Orthomyxoviridae. Questi virus si suddividono in categorie in base alle glicoproteine presenti in superficie: l'emaglutinina (HA) e la neuraminidasi (NA), dalle quali si descrivono 17 e 10 tipi, rispettivamente. La combinazione di un tipo di NA è quello che definisce il subtipo. In questo modo, i subtipi maggioritari nei suini sono l'H1N1, l'H1N2 e l'H3N2.
In base ai diversi studi realizzati in Europa, possiamo affermare che la sieroprevalenza dei 3 subtipi (H1N1, H1N2 e H3N2) è molto elevata nei paesi con vocazione alla suinicoltura. Per esempio, in Germania, Belgio, Danimarca o Spagna, la sieroprevalenza dei 3 subtipi è superiore al 30%. Nel dettaglio, in Spagna, il 94% degli allevamenti sono positivi ad almeno un subtipo. In Francia o Regno Unito si trovano prevalenze elevate di H1N1 o H1N2; tuttavia sembra che l'H3N2 non sia presente, almeno negli ultimi anni. In paesi con minor produzione, come per esempio la Republica Ceca, Irlanda o Polonia, la prevalenza dei SIV sembra essere inferiore.

In un stesso allevamento, è possibile trovare in forma diretta (mediante PCR) o indiretta (mediante inibizione dell'emaglutinazione) più di un subtipo in circolazione. Di fatto, questa situazione è stata dimostrata in Olanda, Francia e Spagna, tra i vari paesi. Individualmente, rimane da dire che la percentuale di suini che presentano anticorpi a più di un subtipo possa essere elevata sia in scrofe sia in suini in ingrasso. Questo fatto suggerisce che l'infezione da SIV è attiva e frequente. Nonostante tutto, la presenza del virus non sempre è associata ad un episodio di malattia respiratoria; infatti, esiste un numero elevato di allevamenti positivi al virus senza sintomatologia apparente. In definitiva, questi riscontri indicano che il SIV si presenta in modo importante come infezione enzootica.
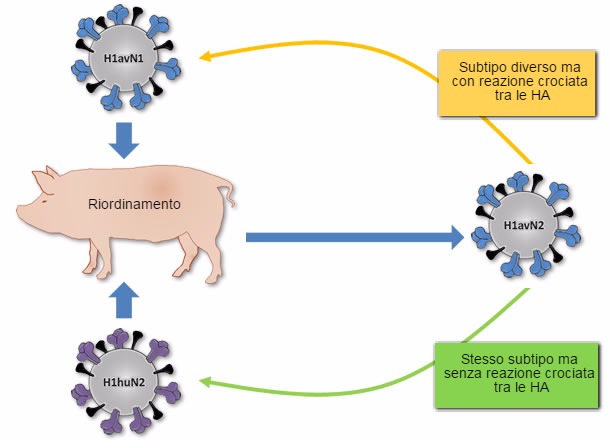
Figura 1. Origine del virus H1avN2 descritto in Danimarca e Francia. Questo virus si genera a partire dal riordine dei virus H1avN1 (che porta la HA) ed il virus H1huN2 (che porta la NA). Come con il virus H1huN2, il H1avN2 appartiene al subtipo H1N2, però su HA non reagirà in forma crociata con questo virus, mentre lo farà con la HA del virus H1avN1, anche se questo appartiene ad un subtipo diverso (H1N1).
La classificazione secondo i subtipi è utile per poter semplificare e comprendere l'epidemiologia e la diversità dei virus influenzali; tuttavia il certo è che la diversità dei SIV è molto più complessa. Come molto bene riassume la Dressa. Simon in un altro articolo pubblicato in precedenza, in Europa, si possono distinguere almeno 4 linee principali in funzione del tipo di HA che contengono. In questa maniera si distinguono quelli correlati con gli H1N1 tipo aviare (H1avN1), quelli correlati agli H1N2 (H1huN2), quelli correlati agli H1N1 endemico (H1N1pdm) e finalmente quelli correlati con gli H3N2.
E' necessario ricordare che i SIV, come qualsiasi altro virus appartenente ai virus influenzali tipo A sono composti da un genoma segmentato in 8 frammenti di RNA il quale gli permette di evolvere attraverso 2 meccanismi: 1) la derivazione antigenica; mutazioni che quando prodotte in appositi luoghi dell'HA (principalmente) o dell'NA possono generare varianti virali che scampano all'immunità creata in precedenza nella popolazione da virus ancestrali (causa principale dell'Influenza stagionale nell'uomo),e 2) il riordinamento genetico, il quale si produce quando 2 o più virus intercambiano frammenti di RNA (per esempio, la generazione dell'anno 1994 del ceppo H1huN2, risultante dal riordinamento tra l'H1N1 umano ed l'H3N2 suino).
Nonostante i 3 H1 distinti (H1avN1, H1huN2, e H1N1pdm) abbiano avuto un ancestrale comune in qualche momento, non si incrociano a livello antigenico o lo fanno in modo limitato.Probabilmente questo è dovuto ai tre H1 che sono evoluti per derivazione antigenica in modo isolato in 3 specie differenti prima di introdursi nel suino in Europa; nei volatili l'H1avN1, nell'uomo l'H1huN2, e nei suini nel NordAmerica l'H1N1pdm. Da un altro lato, il riordino genomico può generare nuovi ceppi virali dell'Influenza, che appartenendo ad un subtipo possono incrociarsi antigenicamente con virus appartenenti ad altri subtipi. Un chiaro esempio è quello del ceppo H1avN2 descritto in Danimarca e Francia. Questo ceppo contiene una HA associata ai ceppi H1avN1 e di conseguenza non si incrocia antigenicamente con il ceppo H1huN2, ma lo fa con i ceppi H1avN1.
La diversità genomica ed antigenica dei virus dell'influenza devono essere compresi come qualcosa di dinamico e con evoluzione costante. I lavori realizzati in Germania, Danimarca, Spagna o Italia, recentemente pubblicati, lo dimostrano. In questi studi sono stati isolati nuovi ceppi risultanti dal riordino tra i ceppi suini di SIV e ceppi dell'Influenza stagionale dell'uomo. Per tutte queste ragioni, è di vitale importanza stimolare una costante vigilanza epidemiologica attiva nei confronti del SIV con l'obiettivo di conoscere i ceppi presenti nella popolazione suinicola, così come la sua prevalenza ed impatto sulla produzione.



